肿瘤治疗-微管靶向库
Tubulin Library From Enamine
微管蛋白靶向库采用了多种方法结合设计而成,包括分子对接、子结构与相似性分析、拓扑类似物搜索、分子参数限制以及特别开发的结构筛选过滤器。
微管蛋白库包含3200个化合物。
https://enamine.net/compound-libraries/targeted-libraries/tubulin-targeted-library
- 陶术生物的所有产品和服务仅用于科学研究,我们不为任何个人用途提供产品和服务。

产品编号: EN4200
- 规格
- 1 mg
- 100 μL x 10 mM (in DMSO)
- 250 μL x 10 mM (in DMSO)
化合物库咨询特别折扣,等您来咨询!
技术资料
产品描述
- 产品描述:
库设计
最近记录在PDB中的蛋白质结构经分析被认为最适合用于计算机筛选,包括4YJ2、5C8Y和5CA1。这三种微管蛋白结构在结合位点处的蛋白质-配体相互作用的主要特征非常相似,可以进行叠加。因此,基于结合口袋中关键氨基酸残基的特征以及在分析的蛋白质结构中观察到的配体相互作用,构建了蛋白质对接模型。
该对接模型已通过一组已知活性配体(110个)和非活性分子组成的参考集进行了验证。根据参考化合物组的活性情况,对分子查询和对接约束条件进行了校正。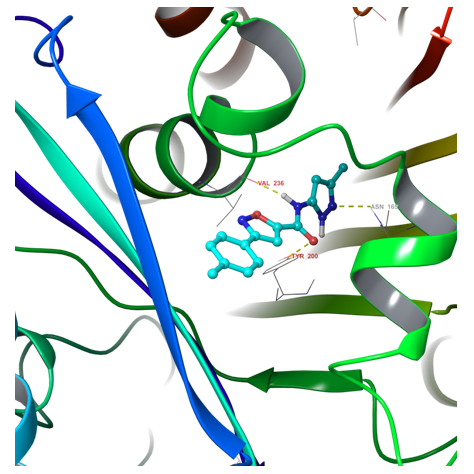
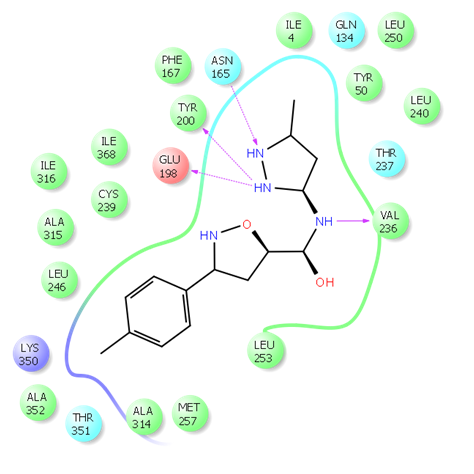 图1. 分子对接计算后命中结合构象确认示例。 图2. 高对接得分先导化合物Z666232790的二维配体相互作用图
图1. 分子对接计算后命中结合构象确认示例。 图2. 高对接得分先导化合物Z666232790的二维配体相互作用图二维相似性搜索与拓扑类比搜索
• 参考化合物集是结合文献来源及多个数据库仔细编制而成,包括:ChEMBL、BindingDB 和 PubChem。
• 化合物筛选采用 95%–80% 的 Tanimoto 相似度区间。
• 通过拓扑场和生物电子等排体替换方法,对活性最强的微管蛋白抑制剂进行类似物搜寻。活性分子举例
通过这种方法筛选出了约900种化合物。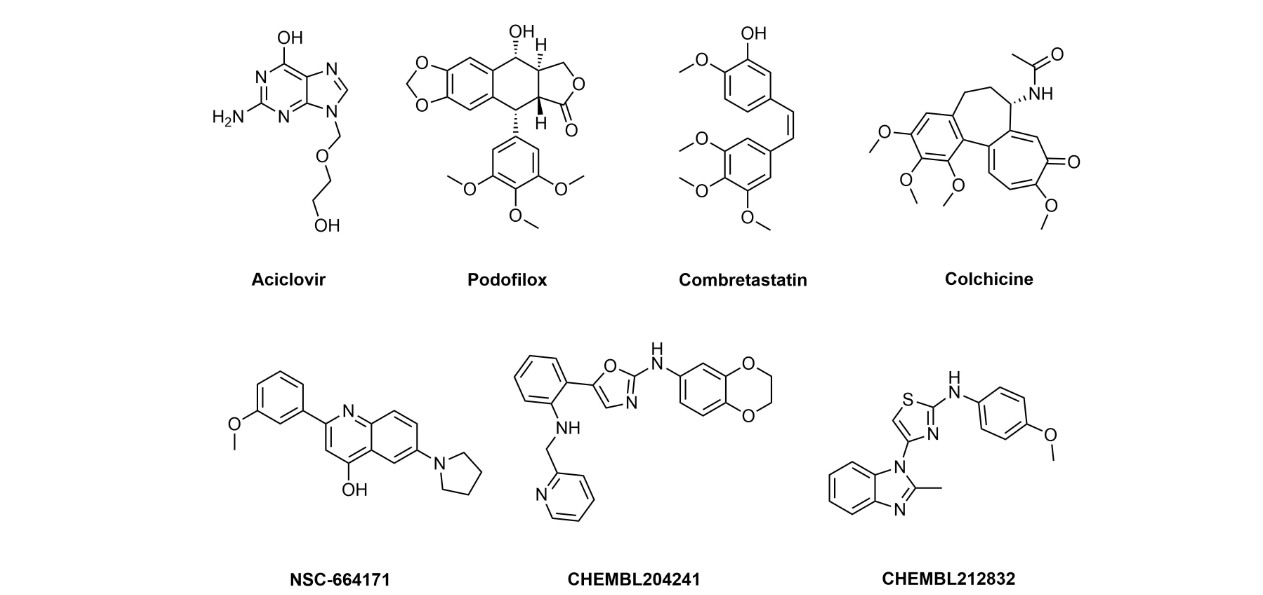
微管蛋白靶向化合物库中的分子示例
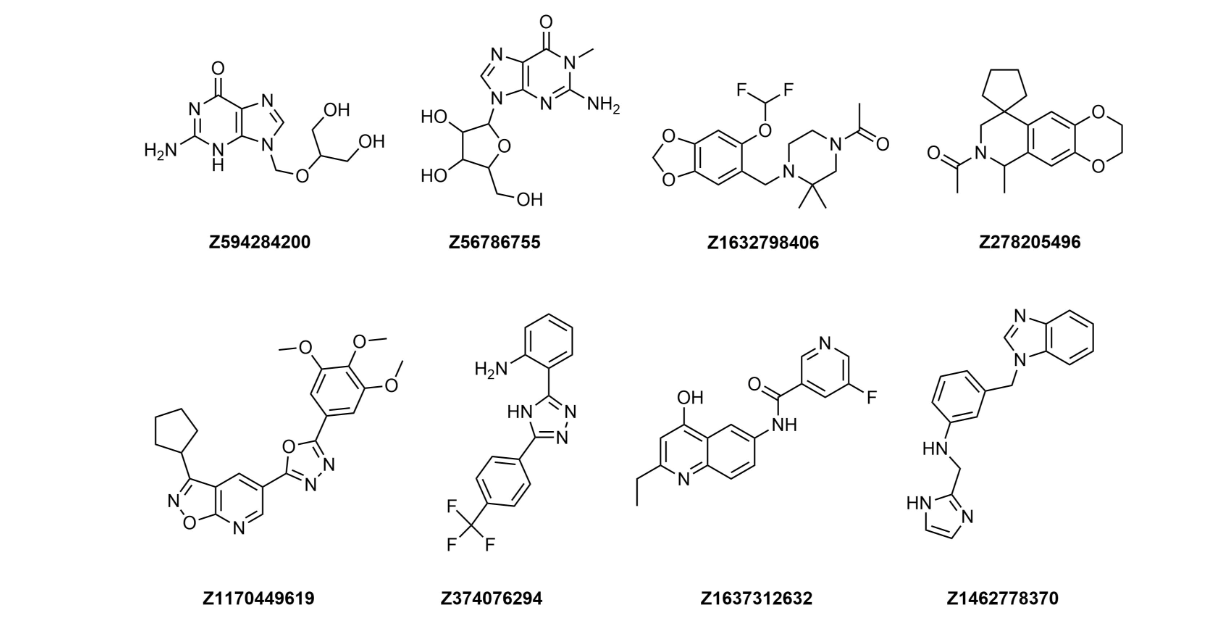
应用于化合物库的筛选标准
• 通过内部研发的药用化学过滤器排除不理想的结构片段,作为Enamine化合物库库存的预筛选步骤。
• 应用了PAINS、礼来、REOS及常规官能团过滤器。
• 完全符合“类药五原则”。 - 包装和储存:
- 可选用DMSO耐受的96/384孔板或2D 条形码编码管;
- 干粉蓝冰运输,DMSO溶液干冰运输;
- 排布:96孔板:1st & 12th 空白对照,384孔板:1st & 2nd & 23th & 24th空白对照。
化合物库定制
我们的化合物库可以灵活定制! 了解更多>
选择化合物
数量
排列
浓度
规格
完成
您可以通过点击按钮
定制您专属的化合物!
寻找合适的化合物库
您无法确定哪种化合物库最适合您的项目?或者您需要定制解决方案?Anymol随时为您提供帮助。
电话:400-820-0310
合作:info@screeningcompound.com
技术支持:tech@screeningcompound.com
客服:service@screeningcompound.com

正在加载 ~
 陶术生物化合物库目录 (78 MB)
陶术生物化合物库目录 (78 MB)  库化合物信息
库化合物信息 Excel
Excel